시작하며
오늘로 통계학 내용은 마무리가 되었다. 정말 어렵고 복잡한 내용이 많았지만 묘하게 재미가 있어서 이후에 강사님께서 추천해주신 책을 구매해서 통계학도 공부해보고 싶다.
영향점
- 스튜던트 잔차 : y중심
- 레버리지 : x중심
- 쿡의 거리 : 쿡의 거리가 4/n(행 개수)보다 큰 관측값을 영향점으로 의심 할 수 있음
aug = hds.stat.augment(model=model)fitted: 추정값resid: 잔차hat: 레버리지sigma: 해당 관측값 제거한 후 표준편차 추정값cooksd: 쿡의 거리std_resid: 표준화 잔차
sigma가 작을수록,cooksd가 클수록 해당 관측값을 이상치로 판단
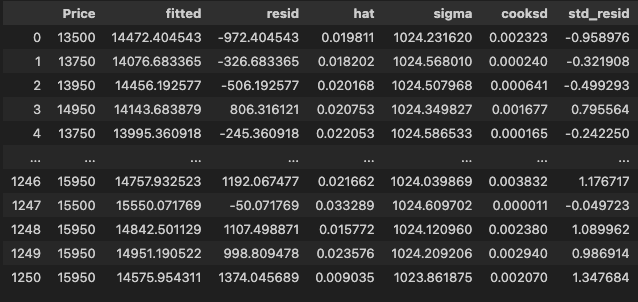
- 이상치 값 인덱스 추출
out_index = aug.loc[aug['cooksd'].gt(4 / X.shape[0])].index- 영향점 시각화
plt.figure(figsize=(4, 4))
sns.regplot(
data=df, x='Age', y='Price', ci=None,
scatter_kws={'color': '0.8', 's': 10, 'ec': '0.8'},
line_kws={'color': 'red', 'lw': 1.5}
)
sns.scatterplot(
data=df.loc[out_index, :], x='Age', y='Price',
fc='red', ec='red', s=20, label='Outlier'
)
plt.legend()
plt.show()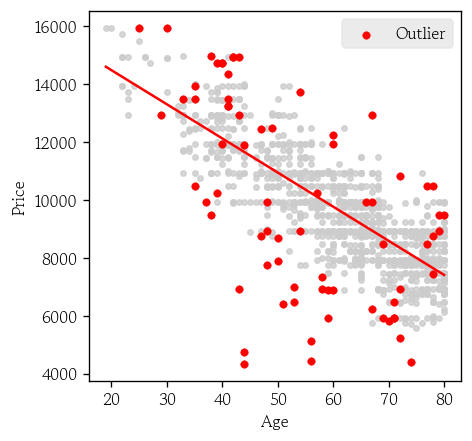
- 영향점 제거
X = X.drop(index=out_index)
y = y.drop(index=out_index)- 영향치 제거한 모형
model = hds.stat.ols(X=X, y=y)
model.summary()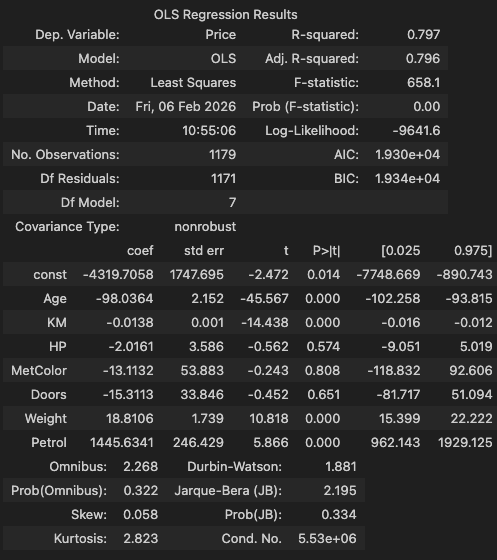
stats.shapiro(model.resid)
# ShapiroResult(statistic=np.float64(0.9987108551069022), pvalue=np.float64(0.5564148139317799))
hds.stat.breushpagan(model=model)
# Statistic P-Value F-Value F P-Value
# 0 14.124654 0.049008 2.028417 0.048685다중공선성
변수 ⬆️ → ⬆️ → MSE ⬇️
변수 ⬇️ → ⬇️ → MSE ⬆️
- 입력변수 간 강한 상관관계가 있으면 다중공선성문제가 발생
- 강한 상관관계를 갖는 입력변수들은 목표변수에 대한 설명력을 나누어 가져 신뢰할 수 없게 됨
- 회귀계수의 표준오차가 증가 → 회귀계수의 설명력 낮아짐
분산팽창지수(VIF)
- 다중 선형 회귀 모형에서 입력변수가 다른 입력변수에 종속 여부를 판단할 때 계산
- 각 입력변수를 목표변수로 설정하여 나머지 변수들로 모형 적합
- 결정계수 0.8 → VIF 5
- 결정계수 0.9 → VIF 10
- VIF가 5 이상이면 다중공선성 문제가 있을 가능성 있음
- 10 이상이면 매우 심각한 문제가 있다고 판단
다중공선성 확인
hds.stat.vif(model=model)
# Age KM HP MetColor Doors Weight Petrol
# 0 1.335567 1.609369 3.123682 1.015065 1.633648 4.762933 6.615611- 다중공선성 문제 해결
X = X.drop(columns='Petrol')
model = hds.stat.ols(X=X, y=y)
hds.stat.vif(model=model)
# Age KM HP MetColor Doors Weight
# 0 1.333597 1.498871 1.13305 1.013634 1.279331 1.457494변수선택법
- 입력변수의 모든 경우의 수를 고려하여 성능이 우수한 최종 회귀 모형을 선택
- 입력변수가 p개일 때 → 개의 후보 모형을 생성해야 함
- 전진선택법, 후진소거법, 단계적방법으로 적합
- AIC가 가장 작은 모형을 선택
AIC
- 모형의 적합도와 복잡도를 고려한 평가 지표
- 모형의 적합도 : 최대 가능도
- 복잡도 : 모형에 사용된 변수의 개수
- 오차항이 정규분포를 따르면, 최대 가능도는 잔차제곱합으로 표현
- AIC 값이 작을수록 좋은 모형이라고 판단
- 좋은 변수 → AIC ⬇️
- 나쁜 변수 → AIC ⬆️
전진선택법
- 입력변수를 하나씩 추가하면서 최적의 회귀 모형을 탐색
- Null 모형에서 입력변수를 하나씩 추가 → 그 중에서 AIC가 가장 작은 후보 모형을 선택
- 이전 단계 회귀 모형보다 AIC가 작은 후보 모형이 없으면 중단
- 최대 개 후보 모형을 적합
- 한 번 선택한 입력변수를 제거할 수 없음
- Null 모형에서 입력변수를 하나씩 추가 → 그 중에서 AIC가 가장 작은 후보 모형을 선택
후진소거법
- 입력변수를 하나씩 제거하면서 최적의 회귀 모형을 탐색
- Full 모형에서 입력변수를 하나씩 제거 → 그 중에서 AIC가 가장 작은 후보 모형을 선택
- 최대 개 후보 모형을 적합
- 한 번 제거한 입력변수를 추가할 수 없음
- Full 모형에서 입력변수를 하나씩 제거 → 그 중에서 AIC가 가장 작은 후보 모형을 선택
단계적방법
- 전진선택법과 후진소거법의 단점을 보완한 방법
- Null 모형에서 입력변수를 하나씩 추가 또는 제거한 후보 모형을 적합 → 그 중에서 AIC가 가장 작은 후보 모형을 선택
- 가장 성능 좋은 회귀 모형을 탐색할 수 있지만 적합해야 할 후보 모형 개수가 많음
- Null 모형에서 입력변수를 하나씩 추가 또는 제거한 후보 모형을 적합 → 그 중에서 AIC가 가장 작은 후보 모형을 선택
model = hds.stat.stepwise(X=X, y=y, direction='both')
model.summary()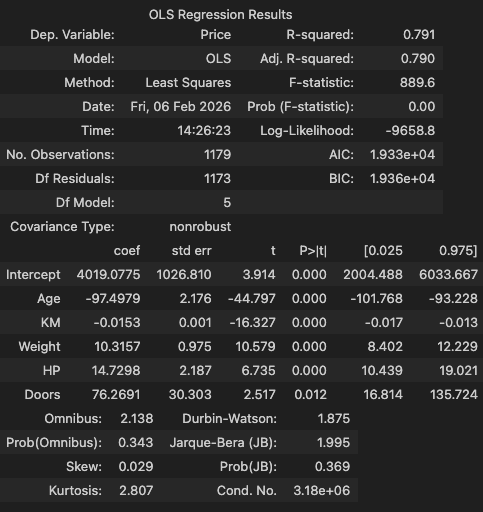
hds.stat.breushpagan(model=model)
# Statistic P-Value F-Value F P-Value
# 0 10.220546 0.069222 2.051491 0.069082로지스틱 회귀
로지스틱 회귀의 개요
- 목표변수가 범주형일 때 사용하는 알고리즘
- 목표변수를 입력변수 간 선형결합으로 표현
- 입력변수마다 목표변수에 영향을 미치는 크기를 제시
- 해석하기 쉬운 모형으로 분류 모형에서 많이 사용
- 0 또는 1인 목표변수를 0~1 사이의 실수로 추정
- 분류 기준점을 설정하여 추정 확률을 추정값으로 변환
로지스틱 회귀의 기본 가정
- 입력변수와 목표변수 간의 관계를 로그 오즈(로짓 함수)로 표현
- 입력변수의 선형결합은 ~
- 목표변수가 이항분포를 따를 때 값을 0~1이 되도록 로짓 변환
- 관측값은 독립성을 유지해야 함
- 잔차의 정규성 및 등분산성 가정 X
로지스틱 회귀 프로세스
탐색적 데이터 분석 → 목표-입력변수 관계 확인 → 회귀계수 추정(가능도 방법 GLM)
→ 유의성 검정(모형, 계수) → 다중공선성 해결(분산팽창지수) → 오즈비 확인(모형 해석)
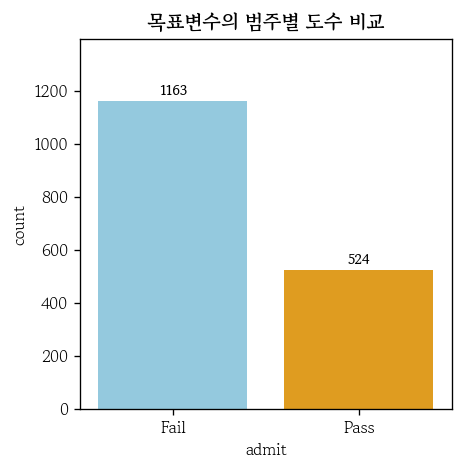
- 목표변수 도수 확인
hds.plot.bar_freq(
data=df, x='admit', palette=['skyblue', 'orange']
)
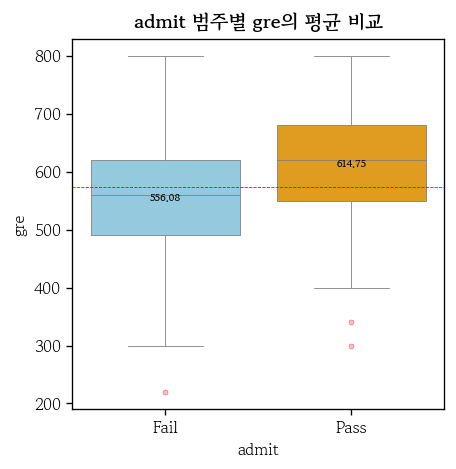
- 입력변수와 관계 확인
hds.plot.box_group(
data=df, x='admit', y='gre',
palette=['skyblue', 'orange']
)
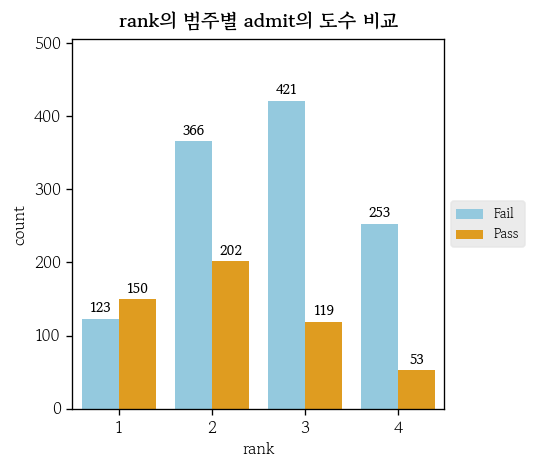
hds.plot.bar_dodge_freq(
data=df, x='rank', g='admit',
palette=['skyblue', 'orange']
)
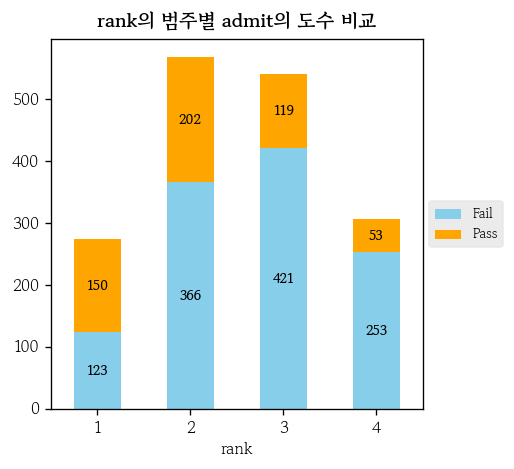
hds.plot.bar_stack_freq(
data=df, x='rank', g='admit',
palette=['skyblue', 'orange']
)
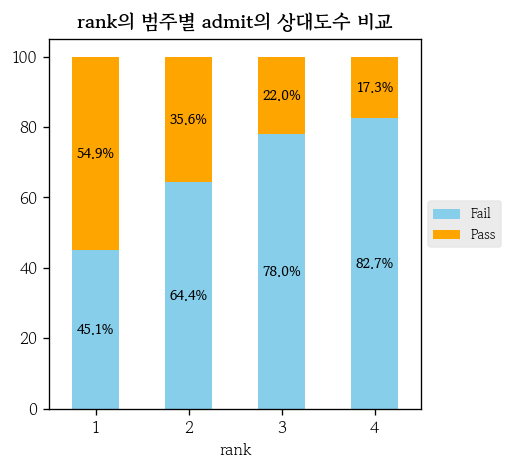
hds.plot.bar_stack_prop(
data=df, x='rank', g='admit',
palette=['skyblue', 'orange']
)
t-검정
pd.pivot_table(
data=df, index='admit', values='gre',
aggfunc=['count', 'mean', 'std'], margins=True
).round(2)
# count mean std
# gre gre gre
# admit
# Fail 1163 556.08 96.36
# Pass 524 614.75 88.92
# All 1687 574.30 97.92pg.normality(data=df, dv='gre', group='admit')
# W pval normal
# admit
# Fail 0.990857 0.000001 False
# Pass 0.992274 0.008138 Falsepg.homoscedasticity(data=df, dv='gre', group='admit')
# W pval equal_var
# levene 3.596208 0.058082 Truey1 = df.loc[df['admit'].eq('Fail'), 'gre']
y2 = df.loc[df['admit'].eq('Pass'), 'gre']
pg.ttest(x=y1, y=y2, correction=False)
교차분석
pd.crosstab(index=df['rank'], columns=df['admit'], margins=True, normalize='index')
# admit Fail Pass
# rank
# 1 0.450549 0.549451
# 2 0.644366 0.355634
# 3 0.779630 0.220370
# 4 0.826797 0.173203
# All 0.689389 0.310611pg.chi2_independence(data=df, x='rank', y='admit')[2]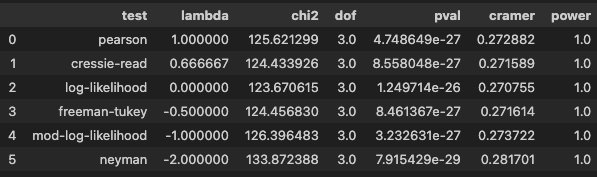
범주형 입력변수의 더미 변수 변환
df = pd.get_dummies(
data=df, columns=['rank', 'admit'],
prefix=['rank', None],
dtype=int, drop_first=True
)
# gre gpa rank_2 rank_3 rank_4 Pass
# 0 380.0 3.61 0 1 0 0
# 1 660.0 3.67 0 1 0 1
# 2 800.0 4.00 0 0 0 1
# 3 640.0 3.19 0 0 1 1
# 4 520.0 2.93 0 0 1 0범주형 입력변수의 더미 변수 변환
yvar = 'Pass'
X = df.drop(columns=yvar)
y = df[yvar].copy()
display(X)
display(y)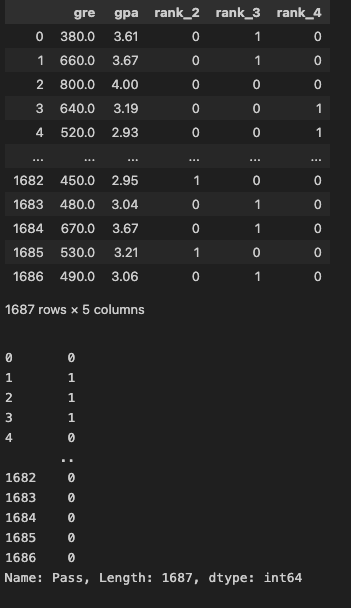
추정 확률 설정
- 입력변수 행렬 X가 주어졌을 때 목표변수가 1일 확률을 p, 0일 확률을 1-p로 설정
- 모든 관측값에 대해 p를 1에 가깝게 추정하는 문제로 변환
오즈
- 실패 확률 대비 성공 확률의 배수
로짓
- 오즈에 로그를 씌운 것을 로그 오즈 또는 로짓이라고 함
- 로짓을 알면 확률을 계산할 수 있음
로짓 변환
- 로짓 함수와 시그모이드 함수는 역함수 관계
- 시그모이드 :
- 로짓은 확률의 로그 오즈를 의미
- 입력변수의 선형결합과 같다고 가정
- 확률과 선형결합을 연결할 수 있으므로, 확률 추정 문제로 적용 가능
최대가능도 추정법
- 서로 독립적인 사건이 함께 발생할 확률은 모두 곱함
- 양변에 자연로그를 씌우면 곱셈을 덧셈으로 변형
로지스틱 회귀 모형의 가능도 함수
- y = 0, p = 1-p
- y = 1, p = p
로지스틱 회귀계수 추정 : 최대가능도 추정법
- 이 함수를 최대로 만드는 회귀계수 를 추정
로지스틱 회귀 적합 함수
- 목표변수는 이항분포를 따름
- 일반화 선형 모형(GLM)으로 적합
model = hds.stat.glm(X=X, y=y)
model.summary()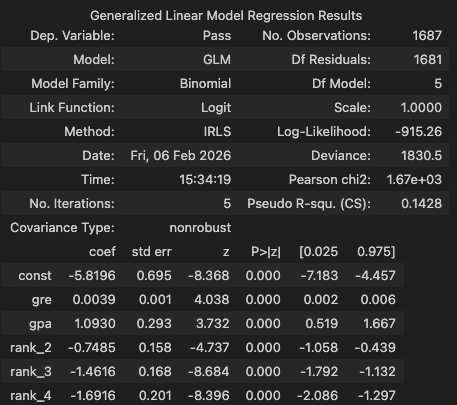
Deviance: 모형 검정(카이제곱)Pseudo R-squ: 유사 계수
로지스틱 회귀 모형의 유의성 검정
- 입력변수를 추가한 residual 모형과 입력변수가 없는 null 모형 간 유의한 차이가 있는지 여부 확인
- 두 모형의 이탈도 차이로 카이제곱 검정을 실행
- 이탈도는 작을수록 로지스틱 회귀 모형의 성능이 좋다는 것
- 두 모형의 성능 차이가 클수록 이탈도의 차이가 증가
- 검정통계량의 자유도는 두 모형의 자유도 차이(입력변수의 개수)로 지정
로지스틱 회귀 모형의 유의성 검정
- 검정통계량과 자유도로 유의확률을 계산
devGap = model.null_deviance - model.deviance
devGap
# np.float64(259.97760909804174)
dofGap = model.df_model
dofGap
# np.int64(5)로지스틱 회귀계수의 유의성 검정
- 유의성 검정은 z-검정 또는 Wald 검정을 이용
1 - stats.chi2.cdf(x=devGap, df=dofGap)
# np.float64(0.0)다중공선성 확인
- 분산팽창지수가 10 이상인 입력변수가 2개 이상 있다면 분산팽창지수가 최댓값인 입력변수 하나만 삭제 → 회귀 모형 다시 적합 후 분산팽창지수 재확인
오즈비
- 오즈비는 두 오즈의 비율
- 오즈를 알면 성공 확률을 계산할 수 있음
- 오즈비는 확률 자체의 변화가 아닌 오즈의 비율 변화
회귀계수를 자연상수가 밑인 지수변환 → 오즈비 얻음
오즈비는 해당 변수가 1 증가할 때 합격 오즈가 몇배인지 나타낸 값
합격 오즈를 알면 확률을 얻을 수 있음
마치며
내일 ADsP 시험을 보고 와서 이번 통계 파트에 대해 쭉 정리를 해봐야 될 것 같다.
